L’observation des systèmes biologiques par microscopie de fluorescence connait une véritable révolution avec l’avènement des techniques de super-résolution optique permettant de dépasser la limite de diffraction, travaux récompensés par le prix Nobel de Chimie en 2014 et le prix Breakthrough en 2018. Le microscope se mue ainsi en nanoscope offrant des échelles d’observation jusque-là inégalées. Cependant différentes limitations restreignaient encore les possibilités d’observations, en particulier sur la dimension axiale où la précision était relativement limitée et applicable uniquement sur une zone restreinte. La persistance de différents biais de mesures ou des problèmes de chromatismes restaient également problématiques.
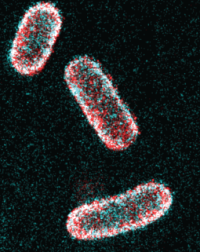
Des physiciens de l’Institut des Sciences Moléculaire d’Orsay (ISMO, CNRS / Université Paris Saclay), de l’Institut Langevin (ESPCI Paris / CNRS) et du centre de Photonique Biomédical (Université Paris Saclay) ont mis au point une technique innovante permettant de déterminer la position axiale des molécules émettrice de façon absolue avec une précision nanométrique. Pour cela, ils ont utilisé une propriété particulière de l’émission de fluorescence à proximité de la lamelle de verre sur laquelle les cellules sont déposées. Cette émission dite supercritique est en plus insensible aux dérives axiales et aux problèmes de chromatisme. En associant cette technique à d’autres méthodes de localisation axiales, ils ont pu étendre les performances de localisation au-delà du premier micron, tout en conservant une mesure absolue et sans biais. En collaboration avec des collègues chimistes (ISCN, CNRS / Université Paris Saclay) et biologistes (INP, CNRS/Université Aix Marseille), cette nouvelle méthode, appelée DAISY, a permis d’observer en 3D différentes protéines du cytosquelette cellulaire, l’insertion d’une sonde fluorescente introduite par « click chemistry » dans des bactéries ou la position de différentes protéines dans des neurones.
Ces résultats, fruit d’une collaboration étroite et fortement interdisciplinaire viennent d’être publiés dans Nature Communications. Ils ont reçu le soutien du Fond AXA pour la recherche, du Labex WIFI, du DIM NanoK et du réseau européen LaserLab. Ces travaux font également l’objet d’un transfert technologique auprès de la société Abbelight, jeune start-up en biotechnologies issue de l’ISMO et de l’Institut Langevin, actuellement incubée à l’ESPCI Paris. De nombreuses recherches en biologie vont ainsi pouvoir bénéficier très rapidement de cette nouvelle technique qui offre des avantages uniques en termes d’imagerie cellulaire 3D.
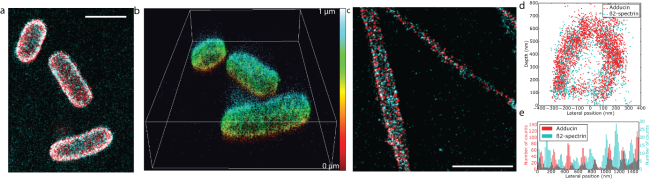
Figure : a) et b) représente une image DAISY en 2D et 3D de bactéries E. Coli marquées par « click chemistry », c) représente l’organisation de l’adducine et la spectrine B2 dans des neurones de rat, d) et e) sont des coupes axiale et latérale de (c) qui confirment l’organisation tubulaire et l’alternance latérale des 2 protéines avec une périodicité de 190 nm.
Référence
Combining 3D single molecule localization strategies for reproducible bioimaging
C. Cabriel, N. Bourg, P. Jouchet, G. Dupuis, C. Leterrier, A. Baron, M.-A. Badet-Denisot, B. Vauzeilles, E. Fort and Sandrine Lévêque-Fort
Nature Communications 10, 1980 (2019)










